Nat Med | Mbinu ya omiki nyingi ya kuchora ramani ya mazingira ya uvimbe uliojumuishwa, kinga na vijidudu vya saratani ya utumbo mpana inaonyesha mwingiliano wa vijidudu na mfumo wa kinga.
Ingawa alama za kibiolojia za saratani ya utumbo mpana zimesomwa kwa kina katika miaka ya hivi karibuni, miongozo ya sasa ya kimatibabu inategemea tu upangaji na ugunduzi wa kasoro za urekebishaji usiolingana wa DNA (MMR) au kutokuwa na utulivu wa microsatellite (MSI) (pamoja na upimaji wa kawaida wa ugonjwa) ili kubaini mapendekezo ya matibabu. Watafiti wamebaini ukosefu wa uhusiano kati ya majibu ya kinga yanayotegemea usemi wa jeni, wasifu wa vijidudu, na stroma ya uvimbe katika kundi la saratani ya utumbo mpana ya Saratani ya Genome Atlas (TCGA) na kuishi kwa mgonjwa.
Kadri utafiti unavyoendelea, sifa za kiasi za saratani ya msingi ya utumbo mpana, ikiwa ni pamoja na saratani ya seli, kinga, stromal, au vijidudu, zimeripotiwa kuhusishwa kwa kiasi kikubwa na matokeo ya kliniki, lakini bado kuna uelewa mdogo wa jinsi mwingiliano wao unavyoathiri matokeo ya mgonjwa.
Ili kuchambua uhusiano kati ya ugumu wa phenotypic na matokeo, timu ya watafiti kutoka Taasisi ya Utafiti wa Kimatibabu ya Sidra huko Qatar hivi karibuni ilitengeneza na kuthibitisha alama jumuishi (mICroScore) ambayo hutambua kundi la wagonjwa wenye viwango vizuri vya kuishi kwa kuchanganya sifa za microbiome na vigeu vya kukataliwa kwa kinga (ICR). Timu hiyo ilifanya uchambuzi kamili wa jenomu wa sampuli mpya zilizogandishwa kutoka kwa wagonjwa 348 wenye saratani ya utumbo mpana, ikiwa ni pamoja na mpangilio wa RNA wa uvimbe na tishu zenye afya za utumbo mpana, mpangilio mzima wa exome, kipokezi cha kina cha seli T na mpangilio wa jeni la rRNA la bakteria la 16S, lililoongezewa na mpangilio wa jenomu nzima ya uvimbe ili kuainisha zaidi microbiome. Utafiti huo ulichapishwa katika Nature Medicine kama "Atlasi jumuishi ya uvimbe, kinga na microbiome ya saratani ya utumbo mpana".

Makala iliyochapishwa katika Tiba Asili
Muhtasari wa AC-ICAM
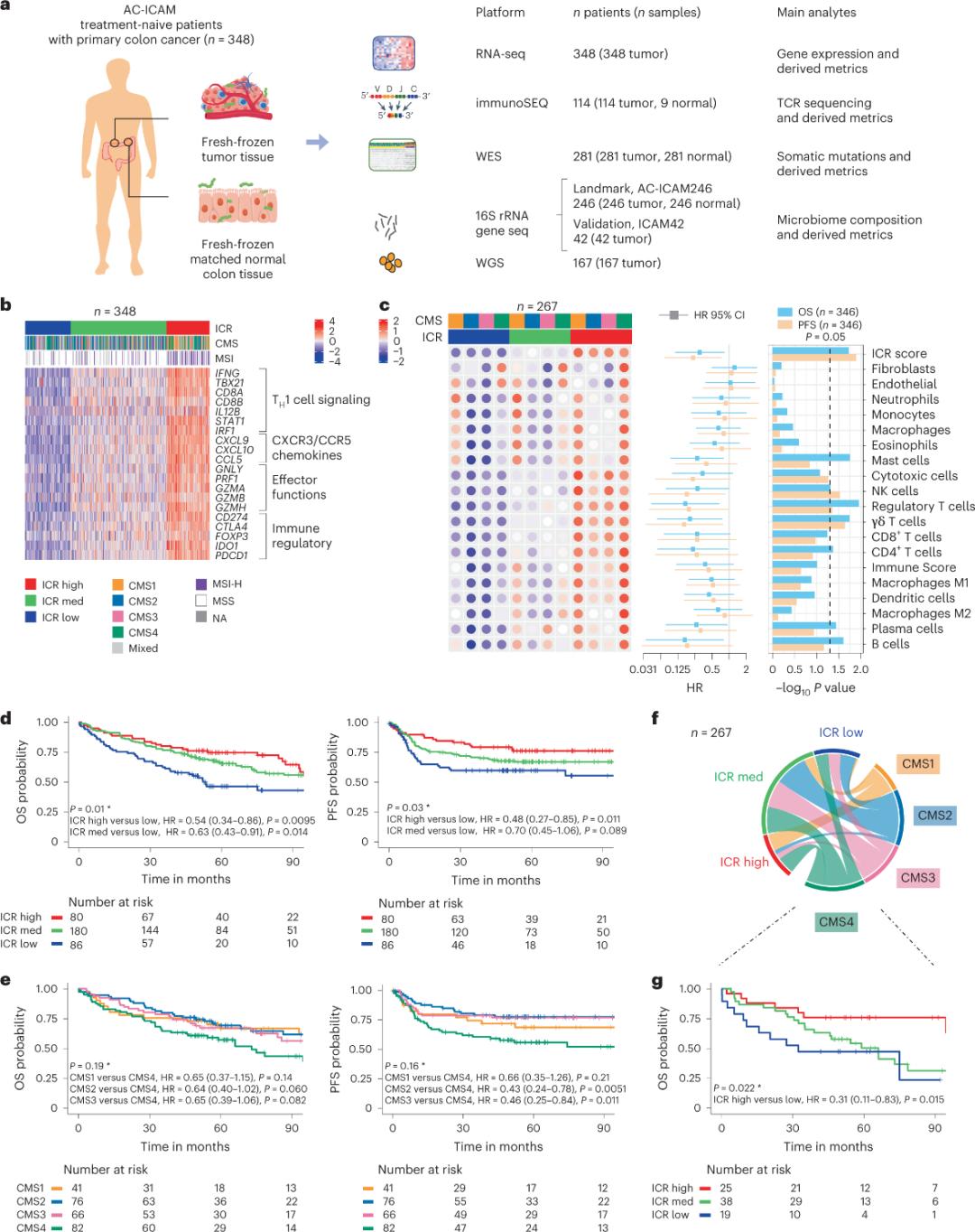
Watafiti walitumia jukwaa la kijenomu la orthogonal kuchambua sampuli mpya za uvimbe zilizogandishwa na kulinganisha tishu za koloni zenye afya zilizo karibu (jozi za uvimbe-kawaida) kutoka kwa wagonjwa walio na utambuzi wa histologic wa saratani ya koloni bila tiba ya kimfumo. Kulingana na mpangilio wa exome nzima (WES), udhibiti wa ubora wa data ya RNA-seq, na uchunguzi wa vigezo vya kuingizwa, data ya kijenomu kutoka kwa wagonjwa 348 ilihifadhiwa na kutumika kwa uchambuzi wa chini kwa ufuatiliaji wa wastani wa miaka 4.6. Timu ya utafiti iliipa rasilimali hii jina Sidra-LUMC AC-ICAM: Ramani na mwongozo wa mwingiliano wa kinga-saratani-vijidudu (Mchoro 1).
Uainishaji wa molekuli kwa kutumia ICR
Kwa kuchukua seti ya moduli ya alama za kijenetiki za kinga kwa ajili ya uchunguzi endelevu wa kinga ya saratani, inayoitwa kinga ya kudumu ya kukataliwa (ICR), timu ya utafiti iliboresha ICR kwa kuipunguza kuwa paneli ya jeni 20 inayofunika aina tofauti za saratani, ikiwa ni pamoja na melanoma, saratani ya kibofu cha mkojo, na saratani ya matiti. ICR pia imehusishwa na mwitikio wa tiba ya kinga katika aina mbalimbali za saratani, ikiwa ni pamoja na saratani ya matiti.
Kwanza, watafiti walithibitisha sahihi ya ICR ya kundi la AC-ICAM, kwa kutumia mbinu ya uainishaji wa pamoja unaotegemea jeni la ICR ili kuainisha kundi hilo katika makundi matatu/aina ndogo za kinga: ICR ya juu (vivimbe vya moto), ICR ya kati na ICR ya chini (vivimbe vya baridi) (Mchoro 1b). Watafiti walibainisha mwelekeo wa kinga unaohusishwa na aina ndogo za molekuli za makubaliano (CMS), uainishaji unaotegemea transcriptome wa saratani ya utumbo mpana. Kategoria za CMS zilijumuisha CMS1/kinga, CMS2/kanoni, CMS3/kimetaboliki na CMS4/mesenchymal. Uchambuzi ulionyesha kuwa alama za ICR zilihusiana vibaya na njia fulani za seli za saratani katika aina zote ndogo za CMS, na uhusiano chanya na njia za kukandamiza kinga na zinazohusiana na stromal ulizingatiwa tu katika uvimbe wa CMS4.
Katika CMS zote, wingi wa seli za muuaji asilia (NK) na seli T ulikuwa wa juu zaidi katika aina ndogo za kinga zenye ICR nyingi, huku kukiwa na tofauti kubwa zaidi katika aina ndogo zingine za leukocyte (Mchoro 1c). Aina ndogo za kinga za ICR zilikuwa na OS na PFS tofauti, huku ongezeko la ICR likiendelea kutoka chini hadi juu (Mchoro 1d), ikithibitisha jukumu la ubashiri la ICR katika saratani ya utumbo mpana.
Mchoro 1. Muundo wa utafiti wa AC-ICAM, sahihi ya jeni inayohusiana na kinga, aina ndogo za kinga na molekuli na uhai.
ICR hunasa seli T zilizoimarishwa na uvimbe na zilizokuzwa kwa njia ya kloni
Ni seli chache tu za T zinazoingia kwenye tishu za uvimbe zimeripotiwa kuwa mahususi kwa antijeni za uvimbe (chini ya 10%). Kwa hivyo, seli nyingi za T za ndani ya uvimbe hujulikana kama seli za T zinazosimama (seli za T zinazosimama). Uhusiano mkubwa zaidi na idadi ya seli za T za kawaida zenye TCR zinazozalisha ulionekana katika idadi ndogo ya seli za stromal na leukocyte (zilizogunduliwa na RNA-seq), ambazo zinaweza kutumika kukadiria idadi ndogo ya seli za T (Mchoro 2a). Katika makundi ya ICR (ujumla na uainishaji wa CMS), ukandaji wa juu zaidi wa TCR za kinga za SEQ ulionekana katika vikundi vya CMS1/kinga vya ICR-high na CMS (Mchoro 2c), huku idadi kubwa zaidi ya uvimbe wa ICR-high. Kwa kutumia transcriptome nzima (jeni 18,270), jeni sita za ICR (IFNG, STAT1, IRF1, CCL5, GZMA, na CXCL10) zilikuwa miongoni mwa jeni kumi bora zinazohusiana vyema na ukandaji wa TCR immunoSEQ (Mchoro 2d). Uhalisia wa TCR wa ImmunoSEQ ulihusiana zaidi na jeni nyingi za ICR kuliko uhusiano ulioonekana kwa kutumia alama za CD8+ zinazoitikia uvimbe (Mchoro 2f na 2g). Kwa kumalizia, uchanganuzi hapo juu unaonyesha kwamba sahihi ya ICR inakamata uwepo wa seli T zilizoimarishwa na zilizokuzwa na uvimbe na inaweza kuelezea athari zake za ubashiri.
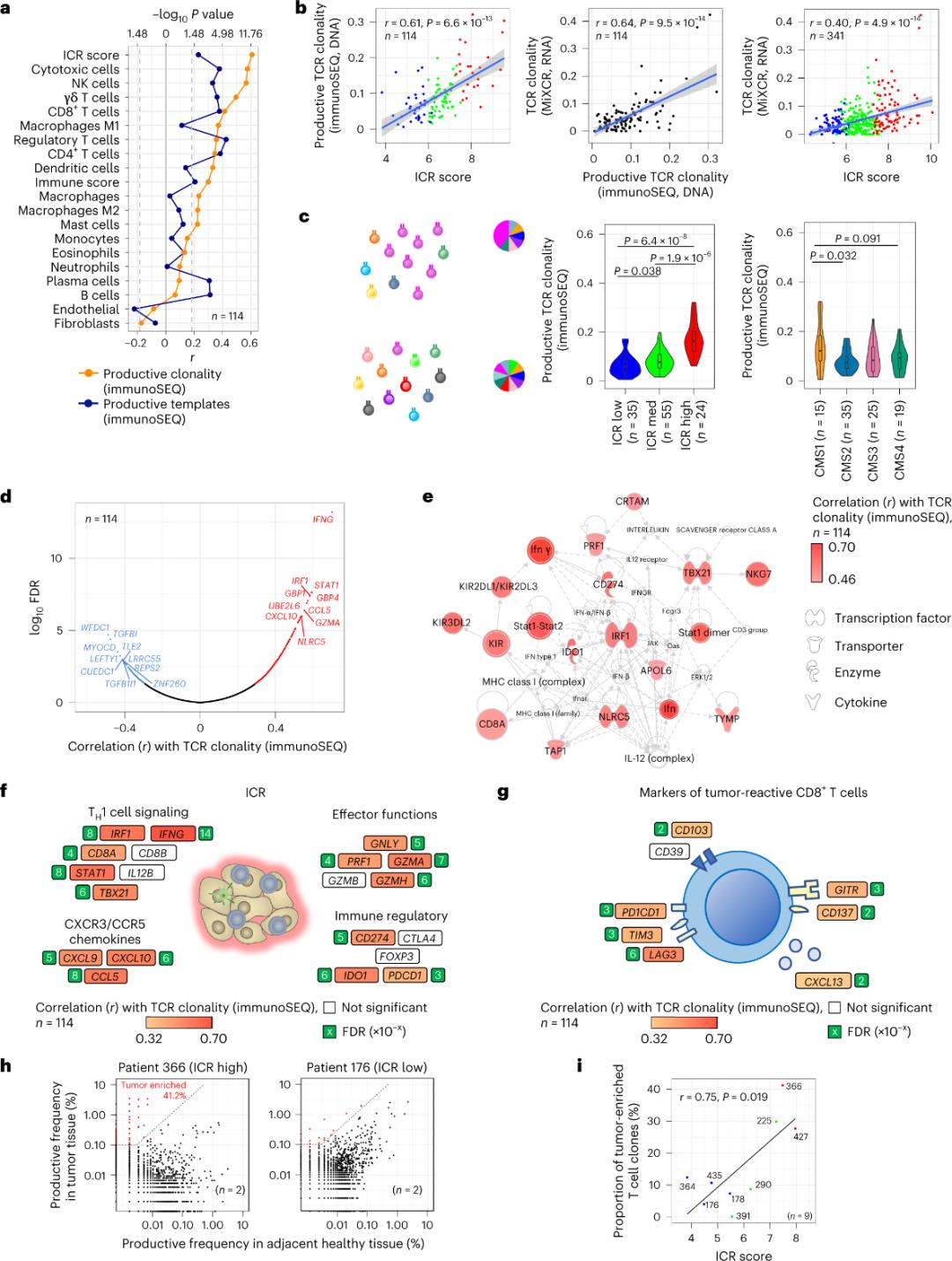
Mchoro 2. Vipimo vya TCR na uhusiano na jeni zinazohusiana na kinga, aina ndogo za kinga na molekuli.
Muundo wa microbiome katika tishu zenye afya na saratani ya utumbo mpana
Watafiti walifanya mpangilio wa rRNA wa 16S kwa kutumia DNA iliyotolewa kutoka kwa uvimbe unaolingana na tishu za utumbo mpana zenye afya kutoka kwa wagonjwa 246 (Mchoro 3a). Kwa uthibitisho, watafiti walichambua pia data ya mpangilio wa jeni la rRNA la 16S kutoka kwa sampuli 42 za ziada za uvimbe ambazo hazikuwa na DNA ya kawaida inayopatikana kwa ajili ya uchambuzi. Kwanza, watafiti walilinganisha wingi wa mimea kati ya uvimbe unaolingana na tishu za utumbo mpana zenye afya. Clostridium perfringens iliongezeka kwa kiasi kikubwa katika uvimbe ikilinganishwa na sampuli zenye afya (Mchoro 3a-3d). Hakukuwa na tofauti kubwa katika utofauti wa alpha (utofauti na wingi wa spishi katika sampuli moja) kati ya sampuli za uvimbe na zenye afya, na kupungua kwa kiasi kidogo kwa utofauti wa vijidudu kulionekana katika uvimbe wenye ICR nyingi ikilinganishwa na uvimbe wenye ICR ndogo.
Ili kugundua uhusiano muhimu wa kimatibabu kati ya wasifu wa vijidudu na matokeo ya kimatibabu, watafiti walilenga kutumia data ya mpangilio wa jeni la rRNA la 16S ili kutambua vipengele vya vijidudu vinavyotabiri uhai. Katika AC-ICAM246, watafiti waliendesha modeli ya urejeshaji ya OS Cox ambayo ilichagua vipengele 41 vyenye viambato visivyo na sifuri (vinavyohusiana na hatari tofauti ya vifo), vinavyoitwa viainishaji vya MBR (Mchoro 3f).
Katika kundi hili la mafunzo (ICAM246), alama ya chini ya MBR (MBR<0, MBR ya chini) ilihusishwa na hatari ya chini sana ya kifo (85%). Watafiti walithibitisha uhusiano kati ya MBR ya chini (hatari) na OS ya muda mrefu katika makundi mawili yaliyothibitishwa kwa kujitegemea (ICAM42 na TCGA-COAD). (Mchoro 3) Utafiti ulionyesha uhusiano mkubwa kati ya alama za endogastric cocci na MBR, ambazo zilikuwa sawa katika uvimbe na tishu za utumbo mpana zenye afya.
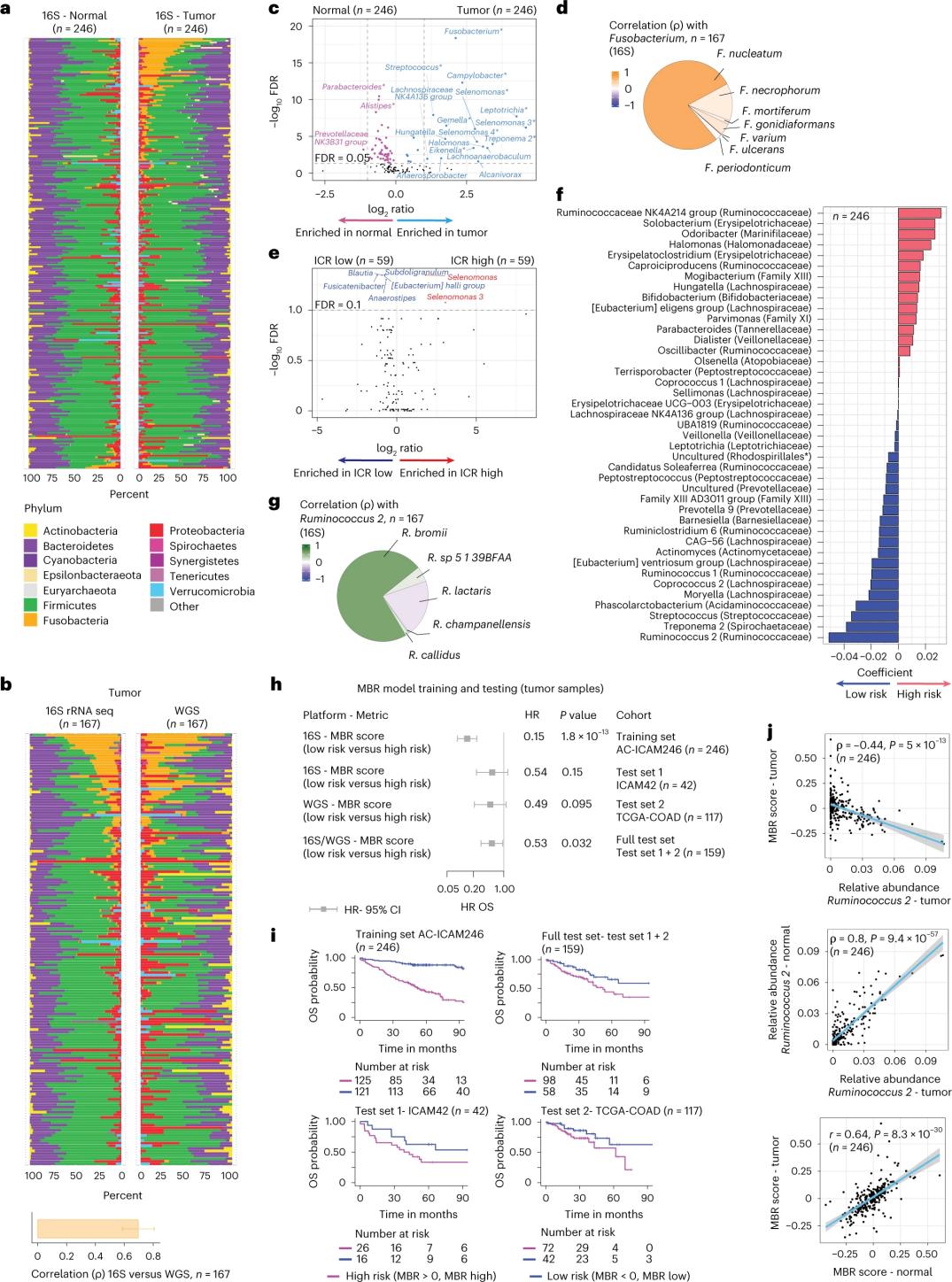
Mchoro 3. Vijidudu katika uvimbe na tishu zenye afya na uhusiano na ICR na kuishi kwa mgonjwa.
Hitimisho
Mbinu ya omiki nyingi inayotumika katika utafiti huu inawezesha kugundua na kuchanganua kwa kina saini ya molekuli ya mwitikio wa kinga katika saratani ya utumbo mpana na inaonyesha mwingiliano kati ya vijidudu na mfumo wa kinga. Mfuatano wa kina wa TCR wa uvimbe na tishu zenye afya ulionyesha kuwa athari ya utabiri wa ICR inaweza kuwa kutokana na uwezo wake wa kunasa kloni za seli T zilizoimarishwa na uvimbe na pengine antijeni maalum ya uvimbe.
Kwa kuchanganua muundo wa vijidudu vya uvimbe kwa kutumia mpangilio wa jeni la 16S rRNA katika sampuli za AC-ICAM, timu ilitambua sahihi ya vijidudu (alama ya hatari ya MBR) yenye thamani kubwa ya ubashiri. Ingawa sahihi hii ilitokana na sampuli za uvimbe, kulikuwa na uhusiano mkubwa kati ya alama ya hatari ya colorectum yenye afya na alama ya hatari ya MBR ya uvimbe, ikidokeza kwamba sahihi hii inaweza kunasa muundo wa vijidudu vya utumbo wa wagonjwa. Kwa kuchanganya alama za ICR na MBR, iliwezekana kutambua na kuthibitisha alama ya alama ya mwanafunzi ya multi-omic inayotabiri kuishi kwa wagonjwa walio na saratani ya utumbo mpana. Seti ya data ya multi-omic ya utafiti huu hutoa rasilimali ya kuelewa vyema biolojia ya saratani ya utumbo mpana na kusaidia kugundua mbinu za matibabu za kibinafsi.
Muda wa chapisho: Juni-15-2023
 中文网站
中文网站